반응형
인터넷이 되지 않는 곳에서 패키지 설치가 어려울때 R에서 생존분석 결과(생명표)만 반출해서 집에서 Survival curve를 그리고 커스터마이징 하는방법
0. 필요한 패키지
library(survival)
library(survminer)
1. 생존분석 결과 반출
fit <- survfit(Surv(time, status) ~ sex, data = lung) #생존분석
res <- summary(fit)
save.df <- as.data.frame(res[c("strata", "time", "n.risk", "n.event", "surv", "std.err", "lower", "upper")]) #생존분석 결과 object를 반출
write.csv(save.df, file = "./Result.csv")
2. 생존분석 결과 object파일 (csv)으로 survival curve 그리기
fit2 <- read.csv("./Result.csv",header=T)
ggsurvplot_df(fit2)
여기서 fit2는 데이터 프레임인데 time: survival time, surv: survival probability, strata: grouping variables, n.censor: number of censors, upper: upper end of confidence interval, lower: lower end of confidence interval 의 변수가 있어야 한다.
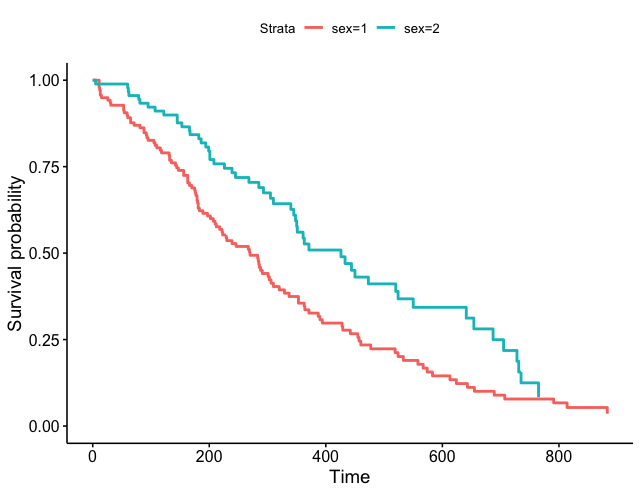
구체적인 커스터마이징은 ggsurvplot의 명령어와 동일한것 같다.
참고 : https://rpkgs.datanovia.com/survminer/reference/ggsurvplot_df.html
'의학통계' 카테고리의 다른 글
| [R] R 기본기 첫번째 (0) | 2019.10.19 |
|---|